LazySlide: accessible and interoperable whole-slide image analysis
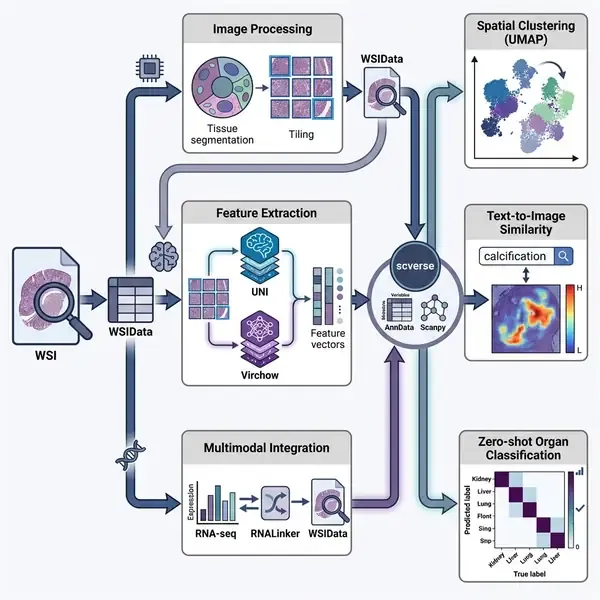
数字病理学领域长期以来一直面临着技术脱节的挑战:尽管全视野数字切片(WSI)提供了无与伦比的空间和形态学见解,但它们在很大程度上仍与单细胞和多模态组学工作流的快速进展相隔离。在《自然-方法》(Nature Methods)发表的一项重要研究中,研究人员推出了 LazySlide,这是一个开源的 Python 框架,旨在通过提供易于访问、可互操作且高性能的 WSI 分析生态系统来弥合这一鸿沟。
LazySlide 的核心是 WSIData 结构,它是 scverse 生态系统 SpatialData 的进化版。与以往因序列化而产生巨大磁盘开销的工具不同,WSIData 实现了对专有 WSI 格式的直接、高效访问,无需数据重复。这一创新使得组织病理学数据能够像单细胞转录组学数据一样,通过编程轻松处理,并遵循 AnnData 和 Scanpy 等广泛使用工具的 API 规范。通过与 scverse 生态系统的无缝集成,LazySlide 将 WSI 从静态图像转变为多模态生物数据集的动态组成部分。
该框架的技术实力源于其对最先进视觉-语言基础模型的整合。LazySlide 支持一套全面的任务,包括自动组织和细胞分割、通过病理专用模型(如 UNI 和 Virchow)进行特征提取,以及无监督空间域检测。值得注意的是,PLIP 和 CONCH 等视觉-语言模型的加入实现了“零样本”能力,允许研究人员使用自然语言提示(如搜索“淋巴细胞”或“钙化”)来查询切片,而无需进行特定任务的训练。
研究人员通过多个高影响力的应用展示了 LazySlide 的实用性。在对 GTEx 项目的人类动脉切片研究中,研究人员利用 LazySlide 计算了“钙化评分”,准确区分了健康组织和病变组织。当与匹配的 RNA 测序数据整合时,该框架揭示了仅靠转录组学无法检测到的分子通路(如 IL-18 信号传导)。此外,该工具在九种不同人类器官的零样本器官分类中表现出卓越的准确性,展示了其在快速、自动诊断支持方面的潜力。
与 QuPath 和 CLAM 等现有工具的基准测试表明,LazySlide 显著降低了代码复杂性和执行时间。它在小鼠乳腺癌模型中实现了更高的分类准确率,并且组织分割的速度明显快于 QuPath 的手动或自动工作流。通过降低技术门槛并促进互操作性,LazySlide 成为计算病理学家和基因组学研究人员的变革性工具,加速了空间分辨率生物标志物的发现以及综合组织生物学模型的发展。